 Nyligen publicerades en artikel i den vetenskapliga tidskriften Nature som presenterar framsteg inom forskningsfältet syntetisk biologi, en disciplin som kombinerar naturvetenskap och ingenjörskonst.
Nyligen publicerades en artikel i den vetenskapliga tidskriften Nature som presenterar framsteg inom forskningsfältet syntetisk biologi, en disciplin som kombinerar naturvetenskap och ingenjörskonst.
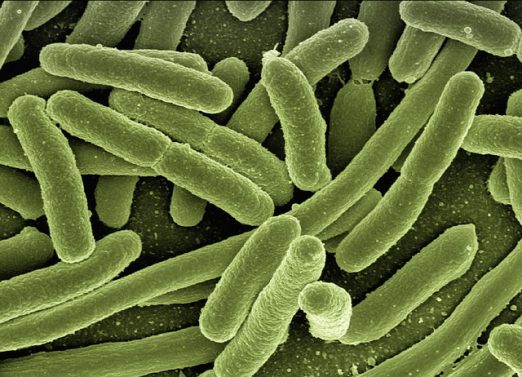
I artikeln beskriver en forskargrupp hur de med syntetiska DNA-molekyler monterat ihop en artificiell arvsmassa med tarmbakterien Escherichia coli (E.coli) som mall. Arvsmassan de tillverkat fördes in i en tom bakteriecell vilket startade upp en proteintillverkning i cellen. Forskarna kunde sedan observera hur den konstgjorda bakterien började växa och dela på sig som vilken annan levande bakterie som helst.
Tidigare har arvsmassor av mindre storlek monterats ihop på liknande sätt med virus och bakterier som mallar. Även delar av en artificiell arvsmassa från den mer komplicerade livsformen jästsvamp har publicerats. Den aktuella studien skiljer sig främst från de tidigare genom att arvsmassan hos E.coli är fyra gånger så stor som den tidigare rekordhållaren. Att tillverka en så stor artificiell arvsmassa och dessutom få den att översättas till proteiner i en tom cell anses vara en stor teknisk bedrift.
Anmärkningsvärt för den aktuella studien är också en bevisligen fungerande arvsmassa monterats ihop utan att alla så kallade kodoner som finns i den genetiska informationen använts. Att en sådan komprimerad version av arvsmassan fungerar säger något om hur formbar den genetiska koden är.
De två dubbelsträngarna i DNA-spiralen är hopbundna av kvävebaserna tymin, cytosin, guanin och adenin (som förkortas T,C,G,A). Tre kvävebaser i följd utgör ett kodon som översätts till en specifik aminosyra. Ordningsföljden av aminosyror bestämmer vilka proteiner som ska tillverkas. Exempelvis så ger kodonet TCA aminosyran serin och TAA fungerar som en stoppsignal som avgör när proteinet är färdigt. Proteinerna bestämmer i sin tur en cells funktion och utgör byggstenarna för allt liv.
Med de fyra kvävebaserna är 64 olika kodoner möjliga. Trots det byggs alla organismer upp av endast 20 olika aminosyror. Det beror på att vissa kodoner översätts till samma aminosyra – något som troligen tillför en dynamik till arvsmassan. På så sätt kan gener enklare fungera som mall för fler än ett protein.
Vid tillverkningen av den konstgjorda bakterien använde forskarna endast 61 av de 64 möjliga kodoner som finns i en vanlig bakterie men fick den ändå att fungera. Det betyder att tre kodoner är ”lediga” och skulle teoretiskt kunna användas till att introducera andra aminosyror än de 20 som bygger upp en organism. Bakterien skulle på så sätt kunna programmeras att tillverka nya proteiner och få nya egenskaper.
E.coli är en bakterie som vi människor satt i arbete inom flera industrier- främst de som baseras på hopfogning av polymerer. Exempelvis så används inom E.coli tillverkningen av insulin och andra läkemedel.
Med de tekniska framsteg som beskrivs i den aktuella artikeln öppnas möjligheter upp för att producera E.coli-bakterier med specifika egenskaper för industriella ändamål. Ett exempel är att designa bakterier som är resistenta mot virus. Det skulle lösa ett återkommande problem inom läkemedelsindustrin där virusinfektioner är ett ständigt hot mot produktionen av för många patienter livsuppehållande mediciner.
/Mia Olsson
Källa: Total synthesis of Escherichia coli with a recoded genome. Nature 15th May 2019.
Mer läsning: Science Express May 20th 2010; Science 328:958 (2010); J. Craig Venter Institute (http://www.jcvi.org/ ); Nature (News) doi:10.1038/news.2010.255 (2010); Nature (Opinion), 465:422 (2010), Dymond et al, Nature 477:471 (sep 2011), Enyeart & Ellington, Nature 477:413 (sep 2011).

